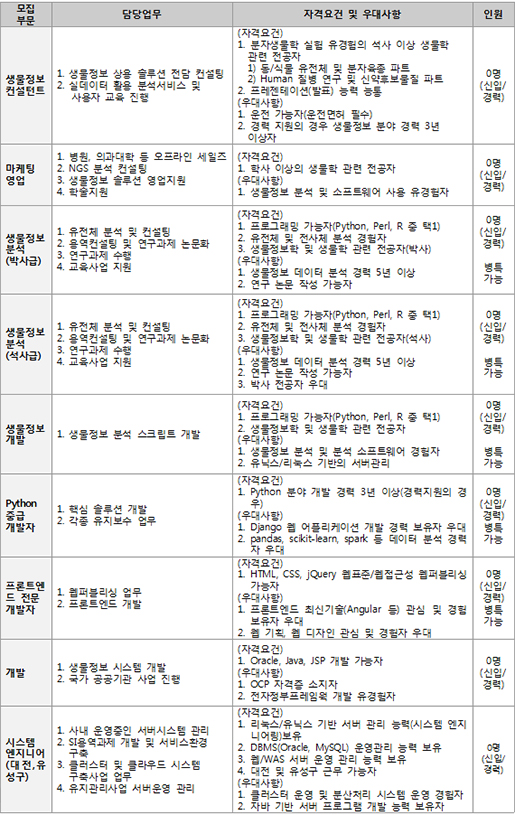
순천향대학교 상민규

생물정보라는 것을 처음 접하게 된 계기는 학부생 때 전공수업인 생물정보학 수업을 통해서였습니다. 익히 알고 있던 실험을 통한 연구가
아닌 Bio와 Informatics라는 융합 학문이라는 것에서 흥미를 느끼고 관련 실험실인 생물정보학 실험실에 들어가 공부하게
되었습니다. 그렇게 공부를 하면서도, 생물정보학이 다른 분야에선 어떻게 이용되는지 모르고 정보를 분석하고 생산해내는 기술들에
대해선 자세히 몰랐습니다. 이러한 것들과 생물정보 기업에 대해 알아보고 경험해보고 싶어 알아보던 와중에 지도교수님께서
㈜인실리코젠이라는 기업을 추천해주셨고, 이를 계기로 人Co INTERNSHIP 프로그램을 지원하게 되었습니다.
인턴십을 진행하는 동안 Planning팀,
Consulting팀, 경영지원실 등의 많은 조직의 업무를 경험해 볼 수 있는 기회가 주어졌습니다. 여러 실무 경험을 쌓을 수
있는 좋은 기회가 되었고, 또한 생각지도 못한 여러 생물정보 분석 프로그램과 Linux, Python 등의 교육을 통해 자신의
능력을 향상시킬 수 있는 계기가 되었습니다. 처음 인턴십을 시작하면서부터 가장 크게 세운 목표가 linux에 대해 배우고 인턴이
끝날 때는 보다 능숙하게 다룰 수 있게 되는 것이었는데, 이번 프로그램을 통해 생물정보 분석 과정과 그 원리 등을 배울 수 있어
알찬 시간이었습니다. 이런 여러 실무 경험과 기본적인 교육, 그리고 분석을 할 수 있는 여러 프로그램 교육들이 앞으로 제가 나아갈
방향을 설정하고, 또 살아가는데 있어 많은 도움이 될 수 있다고 생각합니다.
무엇인가를 완전하게 배우고 몸에 익히기에는 짧은
시간이었지만, 여러 사람들을 만나고 사회 경험을 쌓으며, 저의 능력을 약간이나마 증진시킬 수 있는 소중한 시간이었습니다. 인턴십
기간 동안에 많은 도움을 주신 ㈜인실리코젠의 많은 선배님들과 이런 좋은 기회를 알려주신 지도교수님이신 이용석 교수님, 그리고
인턴십 기회를 주신 최남우 대표이사님께 깊은 감사를 드립니다.
순천향대학교 박종성

인턴십을 하기 전 홈페이지를 처음 접했을 때, 회사 소개에서 '人Co의 핵심가치는 사람을 중심(Core)으로, 사람과
컴퓨터(Computer)에 의해, 배려(Consideration)와 소통(Communication)을 통한 새로운 문화를 창조하는
것이다'라는 문구를 보고, 제가 평소에 추구하고 이상(理想)으로 생각하던, 인간중심의 회사라는 사실에 깊은 감동을 받았었습니다.
이러한 설레는 마음과 배움의 열망을 가지고 ㈜인실리코젠의 人Co INTERNSHIP 프로그램을 시작하게 되었습니다.
먼저 Wiki에 대해 처음 접해보았는데 이것은 제게
하루를 반성하고, 내일을 준비하는, 시간관리와 자기관리를 할 수 있는 기틀을 만들어 주었습니다. 처음에 인상 깊었던 것은
생물정보학 회사임에도 디자인 팀이 있는 것이었습니다. 그 이유가 회사 내부의 문화와 회사가 나아갈 방향을 알아야 그것이 디자인으로
표현되고, 회사의 상황에 따라서 즉각적인 반응을 할 수 있기 때문이라고 하셨습니다. 이것은 제 고정관념을 깨는 큰 가르침이
되었습니다. 또 '독서 경영'과 '집단 지성'을 중심으로 하는 人CoDOM 또한 굉장히 인상 깊고, 좋은 제도라는 생각이
들었습니다. Planning팀에서는, '이러한 기획이라는 일이 있어야, 지금까지 우리나라가 선진국들을 따라하고, 추격하면서 성장을
이루었던 것에서 벗어나서 진정으로 우리가 리드해 나가는 세상을 만들 수 있겠다'라는 생각을 할 수 있었고,
Consulting팀에서는 Pathway Studio의 기본 사용자 메뉴얼을 제작하면서 기본적인 지식을 익히고, 이론 뿐만 아니라
샘플들을 분석해 실습도 같이 해볼 수 있어서 생물정보 분석에 관련하여 공부할 수 있는 좋은 기회였습니다. 또 인턴십 기간 중에 약
2주 동안에 걸쳐 DS 그룹에서 리눅스/파이썬 교육을 받고 실습을 해보면서, 분석에 기본이 되는 컴퓨터 언어들에 관하여
익히고, 활용 능력을 키울 수 있었습니다. 생물정보학을 접해볼 기회가 남들보다 많지 않았었기 때문에, 바로 이해하고 응용하는 것은
어려웠지만, 제가 스스로 공부하고 조금씩 응용하는 것을 익히며 큰 성취감을 느낄 수 있었습니다.
㈜인실리코젠이라는 기업을 겪어보면서, 사람중심의
기업운영, 人CoDOM, Descign 팀 등 정말 까도 까도 계속 벗겨지는 양파 같은 회사라는 생각이 들었습니다. 어쩌면 단순히
경력을 쌓기 위해서, 혹은 경험해보기 위해서 지원했던 이 인턴십은 새로운 분야를 경험하고 제 자신의 장점과 단점 및 새로운
가능성에 대해 확인할 수 있는 좋은 기회였습니다. 아직은 많이 부족하고 당장 남들보다 뛰어나기는 어렵겠지만, 남들보다 한 발 먼저
앞서 시작했다는 것은 분명한 것 같습니다. 항상 존중과 배려를 바탕으로 따뜻한 마음으로 대해주시고, 제게 방향을 제시해 주신
최남우 대표이사님을 비롯한 ㈜인실리코젠의 모든 人Co분들께 다시 한번 감사의 말씀을 드립니다.
부산대학교 박기림

㈜인실리코젠을 처음 알게 된 것은 2014년이었습니다. 당시에 학부 졸업을 앞두고 있던 저는 졸업논문을 작성하는데 있어 ‘CLC
Main Workbench’ 라는 tool 을 접하게 되면서 생물정보학이라는 분야를 처음으로 알게 되었고 관심을 가지게
되었습니다. 2015년 대학원에 진학한 이 후 유전체 정보를 기반으로 한 원예작물 육종을 위한 분자마커 개발을 하게 되었습니다.
현재 연구하고 있는 주제는 다양한 수박 품종들의 전장유전체 재분석을 통하여 품종간 염기서열변이를 탐색하고 유전자 변이와 형질간
연관분석을 수행함으로 실제 분자마커 이용선발 육종에 필요한 정보를 얻는 것입니다. 연구를 진행함에 있어서 생물정보학의 기초부터
유전체 정보의 분석에 대하여 좀 더 자세히 공부하고 싶다는 생각이 들었습니다. 그 때 지도교수님의 추천으로 人Co
INTERNSHIP 프로그램을 접하게 되었고 지원하여 좋은 기회로 약 4주간의 인턴 생활을 할 수 있게 되었습니다. 집이
부산이었기 때문에 한 달 간 회사 근처에서 방을 얻어 생활하게 되었습니다. 첫 출근날 많이 긴장했었는데 대표님께서 좋은 말씀을
많이 해주시고 선배들도 인사를 할 때 웃으면서 받아주시고 챙겨주셔서 감사했습니다. 1
주차에는 회사 생활에 대한 전반적인 교육을 들었습니다. 회사 소개와 사회 생활 등 다양하면서도 기본적인 교육을 듣게 되었습니다.
또한 생물정보 기초교육을 통하여 Linux와 python을 접할 수 있게 되었습니다. 2주차에는 전 주에 배웠던 기본 내용들을
바탕으로 하여 실제 생물정보학 문제를 풀어보는 시간을 가졌습니다. 기본 개념이 부족하다보니 다른 분들처럼 능숙하게 풀지는 못했지만
문제를 제 힘으로 풀었을 때 뿌듯함은 매우 컸습니다. 또한 CLC Genomics Workbench의 튜토리얼을 작성하며
Denovo assembly와 Re-sequencing 등 실제 데이터 분석을 배워볼 수 있었습니다. 첫 주에 미리 말씀을
해주셨던 자기소개발표 시간이 있었는데 많은 사람들 앞에서 제 소개를 하는 것이 익숙치 않아서 긴장을 많이 했었습니다. 발표 내용
중에 저의 장점과 단점을 정리하여 발표하였는데 간단한 슬라이드였지만 그 내용을 채우기 위해서 많이 생각을 할 시간을 가졌던 것
같습니다. 3주차에는 CLC 솔루션 교육을 참관할 수 있는 좋은 기회를 주셔서 튜토리얼 작성때 잘 풀리지 않았던 부분들을 직접
해보고 배울 수 있었습니다. 마지막 주에는 마무리를 할 수 있는 시간을 가졌습니다. 4주간의 人Co INTERNSHIP 과정을
통하여 한 모든 경험들이 제가 앞으로 나아갈 방향에 있어서 큰 도움이 될 것이라고 생각합니다. ㈜인실리코젠, 그리고 대표님을
비롯한 모든 직원 분들과의 좋은 인연에 감사드립니다.
상명대학교 남대근인실리코젠과의 同行

저에게 인실리코젠이 처음 다가왔을 때는 15년도 말에 졸업하신 선배님들의 특강에서였습니다. 졸업을 하시고 사회로 나가는 첫 걸음인 첫
직장에 대한 두려움과 설렘을 사람이 중심인 기업, ‘Personalized Bioinformatics'라는 기치를 중시하는
기업인 인실리코젠을 통해 만족할 수 있었다는 말은 저에게 인실리코젠에 대한 궁금증과 알고자 하는 열망을 심어 주었습니다. 이렇게
인실리코젠은 저에게 다가왔고 저는 인실리코젠과 함께 하고 싶어 人Co INTERNSHIP 2016 동계 프로그램에 지원해 약 한 달
동안 인실리코젠과 동행할 수 있는 기회를 얻었습니다.
첫 주에는 회사소개와 인턴십 프로그램의 설명을 통해 좀
더 인실리코젠을 이해할 수 있었으며, 회사생활에 필요한 다양하고도 기초적인 교육을 받을 수 있는 시간을 가졌습니다. 뿐만 아니라
생물정보를 담고 있는 다양한 데이터를 다루기 위한 Linux와 Python을 교육받을 수 있었는데 이를 통해 저는 앞으로 나아갈
제 삶에 밝은 등불을 얻을 수 있었습니다.
둘째 주에 접어들었을 때는 지난 일주일간 받은 다양한
교육들을 활용할 수 있는 시간을 가졌습니다. Wiki를 활용하여 생물정보 분야의 집단 지성 창출을 목적으로 운영되는 지식
커뮤니티인 人CoDOM에 글을 올렸으며, Linux와 Python을 기초로 좀 더 심화된 생물정보관련 Rosalind 문제들을
풀고, CLC Genomics Workbench를 활용하여 De novo assembly와 BLAST 학습하며 데이터를 다루기
위한 능력을 높일 수 있었습니다.
삼주차 때는 지금까지 갈고 닦았던 프로그래밍 스킬을
통해 NGS 데이터들을 파싱하고 분석하는 시간을 가졌습니다. 다양한 NGS 데이터들의 format들을 다루어 정보를 밝히는 시간은
알지 못했던 방법을 익힐 수 있는 유익한 시간이었습니다.
마지막 주차는 마무리하는 시간을 가졌는데 그동안 학습하였던 것들을 정리하고 다잡을 수 있는 시간이었습니다.
인턴십 프로그램을 처음 접해보았지만 이렇게 알차게
시간을 보낼 수 있다는 것에 정말 감사하다고 생각합니다. 다양한 방법으로 Linux와 Python을 활용하여 데이터들을 다루고
이를 통해 정보를 밝히고자 하는 작업이 저에게는 처음해보는 일이었지만 앞으로 무엇이 필요하고 현재 무엇이 부족한지를 알 수
있었으며 사회 선배들과의 만남을 통해 그분들의 경험과 노하우를 알 수 있었습니다. 마지막으로 인실리코젠과의 동행을 함께 해준 모든
분들께 감사드립니다.
상명대학교 임수정

생물정보학이라는
컴퓨터와 생물학이 합쳐진 학문을 처음 접하고 나서 공부를 하다보니 더 배워보고 싶고 흥미도 생겨서 워크숍도 참석해보고 학교에서
공부도 열심히 하던 중 (주)인실리코젠이란 회사에 대해 처음 접했습니다. 정말 좋은 회사인것 같고, 가고 싶은 마음에 지원서도
써서 내보고 면접도 봐서 3:1의 경쟁률에서 뽑혔습니다. 출근하라는 메일을 받고 얼마나 기뻤는지 아직도 기억이 생생합니다. 첫
출근때 사회생활도 처음이고 학교에서만 지내다가 회사로 나오니까 뭘해야할지 몰라서 어리둥절했던 기억이 납니다.
집이 인천이었음에도 4주동안 한번도 지각을 한 적 없고
저 나름대로 부지런하게 지낸것같아 기분도 좋습니다. 회사를 4주간 다니면서 많은 업무를 하고 교육도 받았습니다. 공통교육을 통해
사회생활 예절과 기본적이지만 많은 도움이 되는 것을 배웠고 정말 만족스럽고 좋았던 교육이었습니다. 데이터분석에 쓰이는 CLC
Genomics Workbench 실습 및 번역, 人CoDOM 작성 및 Linux, Python 등 전반적인 생물정보학 교육을
들었습니다. 또 회사선배님들과도 많은 이야기도 나눠보고 고민상담도 몇번 했었는데 정말 좋으신 말씀 많이 해주셨고 人Co의 가장
중요한 '사람관계'도 많이 배웠습니다.
길면 길고 짧으면 짧은 4주간의 인턴십을 통해 정말
많은 것을 배웠습니다. 생물정보학에 대한 기초와 심화된 내용, 회사에선 어떤 일을 하는지, 생물정보가 어떻게 이용되는지 등 많은
실무경험을 듣고 경험해보았고, 특히 사회생활에 대해 많이 배웠습니다. 4주 동안 제 자신의 부족한 점도 많이 찾게되었고 몰랐던 제
모습도 볼 수 있었고, 인턴분들과 같이 공부도 하고 일도 하고 재미있게 이야기도 많이 나누면서 더 친해진것 같아 사람관계의
중요성도 다시 한번 느끼게 되었습니다. 제 인생에 있어서 인턴십은 절대 잊지못할 추억이자 정말 좋은 경험으로 남을것 같습니다.
이러한 계기로 사회로 나가는 첫 걸음이 헛되지 않게 앞으로도 열심히 공부도 하며 노력할 것입니다.
마지막으로, 바쁘시지만 항상 웃으면서 대해주신 (주)인실리코젠의 최남우 대표님을 비롯한 모든분들께 감사의 말씀 전합니다. 人Co INTERNSHIP이란 프로그램을 통해 정말 많은 것을 배우고 경험하게 해주셔서 감사합니다.

Posted by 人Co

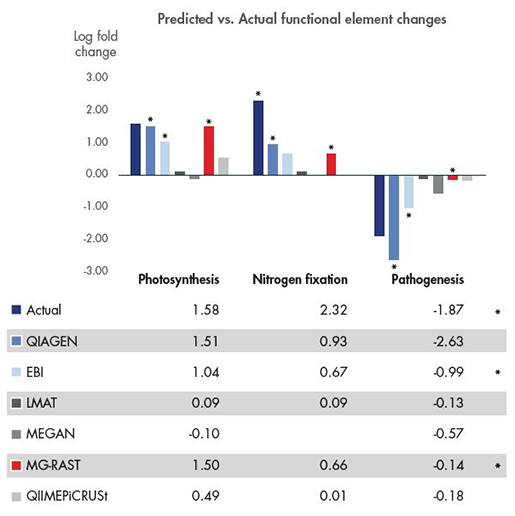
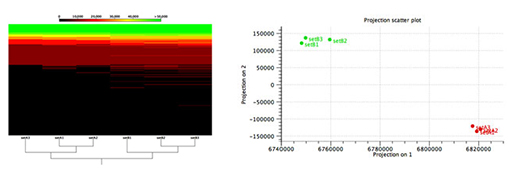
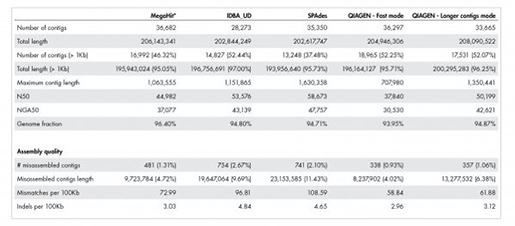
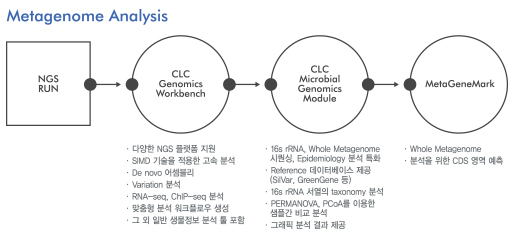
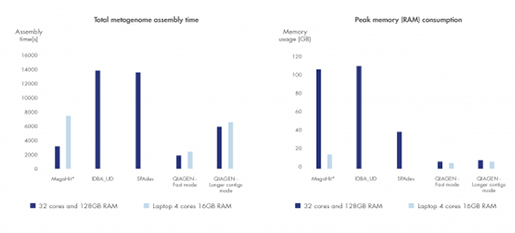 Figure 3. 최고의 metagenome assembly 분석도구
Figure 3. 최고의 metagenome assembly 분석도구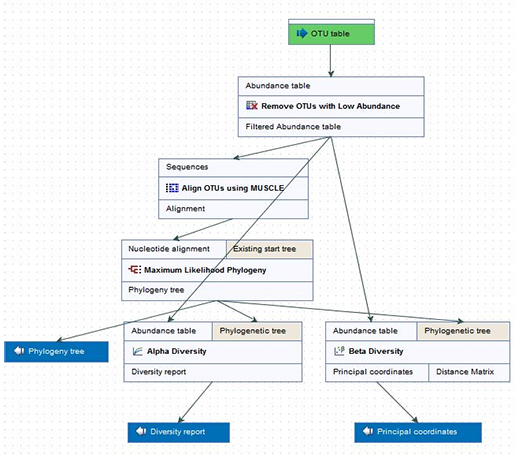










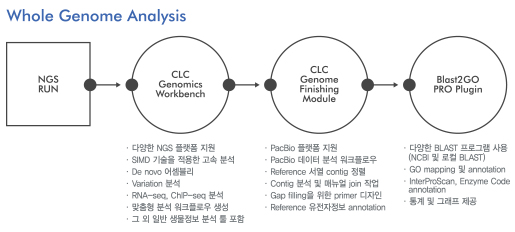

 입사지원서_성명_지원부문.doc
입사지원서_성명_지원부문.doc

 입사지원서_성명_지원부문.doc
입사지원서_성명_지원부문.doc