[LAB.STORY 01] 세종대학교 식품생명공학과 식품 미생물학 및 마이크로바이옴 연구실
- Posted at 2019/02/08 14:58
- Filed under LAB.STORY

CLC Main Workbench는 Bioinformatics 분야에서 염기서열 분석을 위한 가장 기본적인 소프트웨어로 DNA, RNA, Protein, Digital Gene Expression 등의 분자생물학 데이터를 통합 분석 할 수 있습니다. 이러한 생물정보 기초 소프트웨어를 이용하여 대학 강의에 유용하게 활용한 사례를 세종대학교 신학동 교수님께서 공유해 주셔서 소개합니다.
교과 개요
교과명 : 식품분자생물학 및 실험
교수명 : 신학동 교수님
수업 및 실습 장소 : 세종대학교 율곡관 101호 전산 실습실
수업 기간 및 시간 : 2018년도 2학기 월, 수 13:30 ~15:00
교과 목표
이 교과는 식품분자생물학과 관련된 실험적인 방법 및 생물정보학 기술을 학습 및 응용하여 미생물의 생리학, 생화학, 유전체학에 대한 이해를 높이는 것을 목표로 하며 '식품 미생물학 및 실험' 교과를 선수강한 학생들을 대상으로 하는 심화 과정의 교과임.
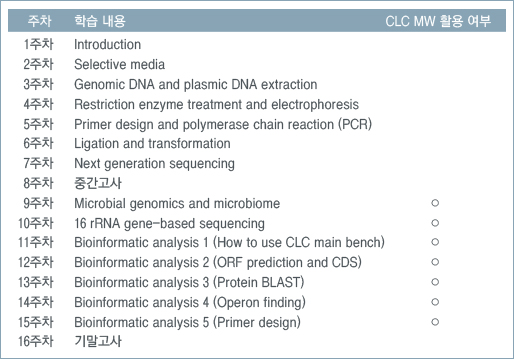
주차 별 학습
교과 진행 방법

대학 전산운영과와 협의를 통해 세종대학교 율곡관 1층에 있는 전산 실습실 사용을 승인받아 학과 차원에서 구매한 라이선스 21대(교수용 1대, 학생실습용 20대)를 사용하여 CLC Main Workbench에 대한 설치를 진행하였으며 학생들의 자리를 사전에 지정하여 프로그램을 운영, 관리하도록 하였음.
교과 진행 방식



[사진 2] 학생 수행 과제물 (실험 노트)
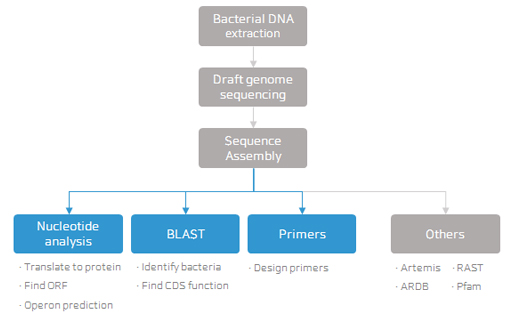 [그림 1] 식품분자생물학 및 실험 수업에서 진행된 분석 모식도
[그림 1] 식품분자생물학 및 실험 수업에서 진행된 분석 모식도학생에게 미지의 bacteria를 제공하고 최종적으로 주어진 bacteria의 학명과 기능을 예측하며 sequence data를 기반으로 target gene을 설정하여 primer를 설계하고 PCR에 성공하는 것을 목표로 함. 이를 위하여 학기 초반 실험을 통하여 미지의 bacteria로부터 genome을 추출하였으며 draft genome sequencing을 진행하였음. sequence file을 assembly 시켜 얻은 ‘.fasta’ 형식의 파일을 사용하여 CLC Main Workbench를 통해 생물통계학 분석을 진행함.
‘Nucleotide analysis’의 하위 기능을 활용하여 ORF(Open Reading Frame)를 예측하고 이 영역을 protein sequence로 변환하여 BLAST를 진행하였음. 이를 통해 CDS(Coding Sequence)의 기능을 예측해낼 수 있었고 총 50개 이상의 CDS를 찾고 기능을 정리하는 과제를 수행하였음. 정리된 CDS 정보를 통해 비슷한 기능을 수행하는 유전자가 모여있는 operon이 존재하는지 예측하는 과정을 거쳤음.
‘Design primers’ 기능을 활용하여 관심 있는 CDS 부분을 증폭시킬 수 있는 primer를 제작하고 최종적으로 학생들이 직접 설계한 primer를 주문 제작하여 PCR(Polymerase chain reaction) 과정을 수행하고 gel electrophoresis를 통해 primer가 적절하게 설계되었는지 확인해보는 과정을 거쳤음.
학생 만족도
전반적인 학생 만족도
학과 특성상, 컴퓨터를 통한 분석의 기회가 많지 않다는 점에서 수업의 내용이 신선하다는 평가가 많았으며 프로그램을 운용하는 데에 어려움을 토로하며 정형화된 학습 교안의 필요성을 언급한 학생도 있었음. 다루고 있는 내용에 비하여 프로그램의 구성 및 조작이 단순하여 분석이 용이했음을 다수가 언급했으며 많은 기능이 한 프로그램 안에 포함되어 있어 편리한 점을 이 프로그램의 가장 큰 장점으로 평가했음.
학생 평가 일부 소개



CLC Main Workbench에 대한 강의를 듣고 직접 진행해 보며 이전에는 이론으로만 접해보았던 부분을 실습해볼 수 있어서 유익했다. 특히 CLC program을 통해서 Primer region을 설정하고 직접 디자인하는 과정이 매우 유용해 기억에 남는다.


Posted by 人Co
- Response
- No Trackback , No Comment
- RSS :
- https://post-blog.insilicogen.com/blog/rss/response/303





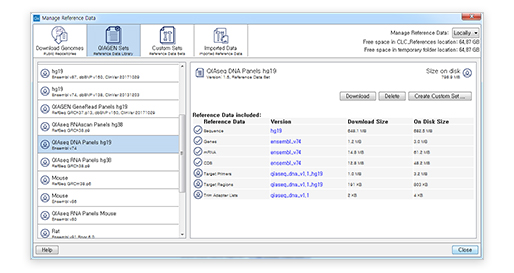 [그림 10] QIAseq 분석에 찰떡인 QIAGEN Sets 다운로드
[그림 10] QIAseq 분석에 찰떡인 QIAGEN Sets 다운로드